Mycobacteria
Líneas de investigación
Content with Investigacion .
Inmunología Microbiana e Inmunogenética
1. Análisis de la respuesta innata de mamíferos en la infección por Leishmania.
2. Caracterización inmunoproteómica en :
a. Streptococcus suis
b. Lactococcus garviae
c. Mycobacterium spp
3. Desarrollo de inmunoensayos analíticos basados en anticuerpos monoclonales (AcM) para detectar y cuantificar antígenos de origen animal, vegetal y microbiano.
4. Desarrollo y caracterización de AcM frente a los componentes del sistema del Complemento. Aplicación diagnóstica.
5. Desarrollo de reactivos de referencia y diseño de inmunoensayos para la evaluación cualitativa y cuantitativa de toxinas clostridiales.
6. Oferta tecnológica de producción de AcM y policlonales frente a substancias de interés industrial y biomédico.
El grupo está interesado en el estudio de la respuesta inmune desde una perspectiva multidisciplinar que incluye aproximaciones bioquímicas, biotecnológicas, genómicas, inmunoinformáticas y proteómicas, que junto con el uso adicional de modelos in vivo se encaminan al diseño de estrategias terapéuticas frente a diversas enfermedades crónicas, infecciosas y raras que poseen un claro componente inmunológico en su etiología.
Las principales líneas de investigación que está desarrollando el grupo en la actualidad son:
- * Análisis de las respuestas inmunes celulares frente a patógenos virales y bacterianos, mediante técnicas inmunoproteómicas, modelos in vivo con animales transgénicos y muestras humanas.
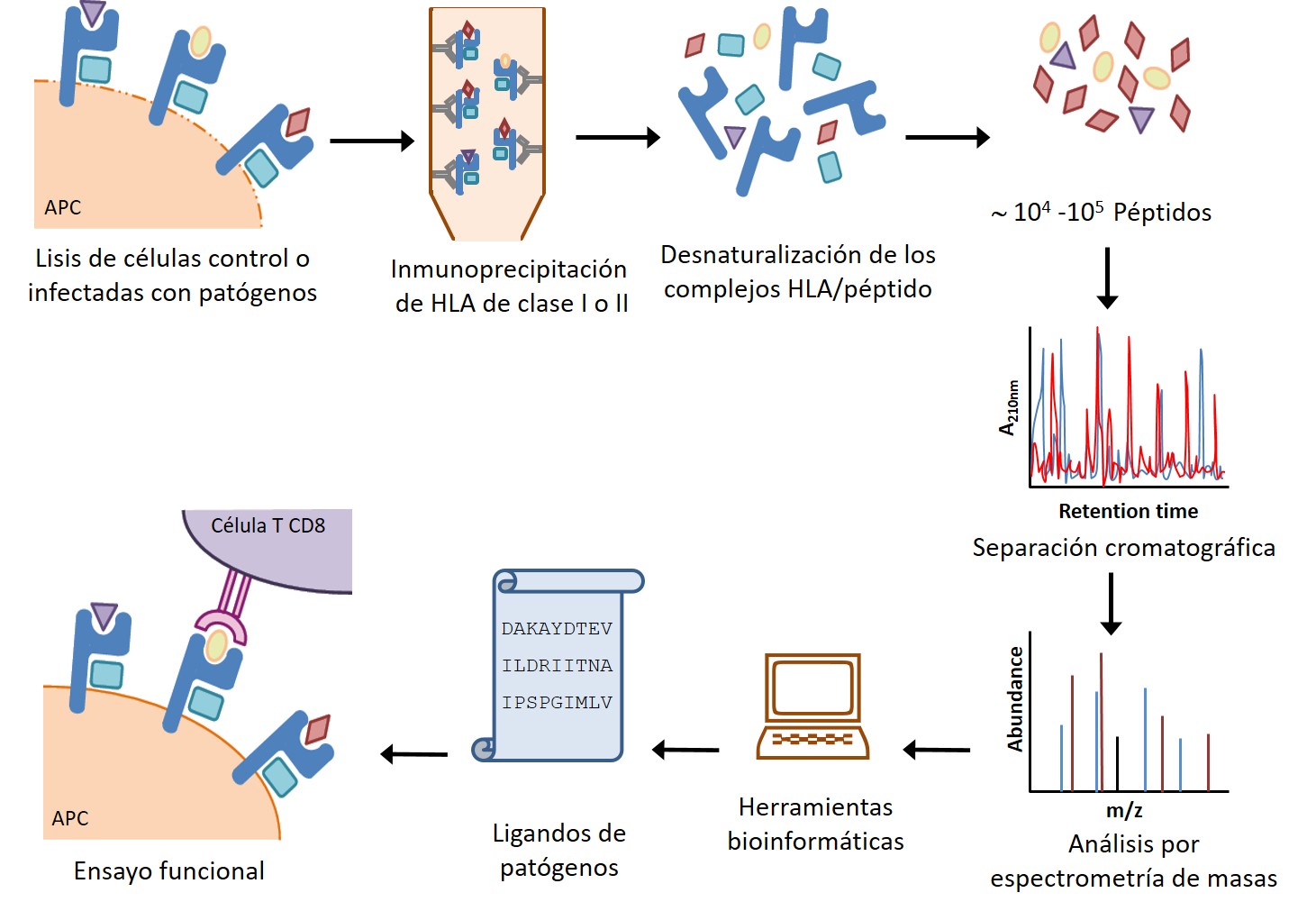
- * Caracterización de CD69: regulación génica, función reguladora inmune en homeostasis e infección y su uso como diana terapéutica, edición génica por CRISPR en modelos animales y celulares, etc.

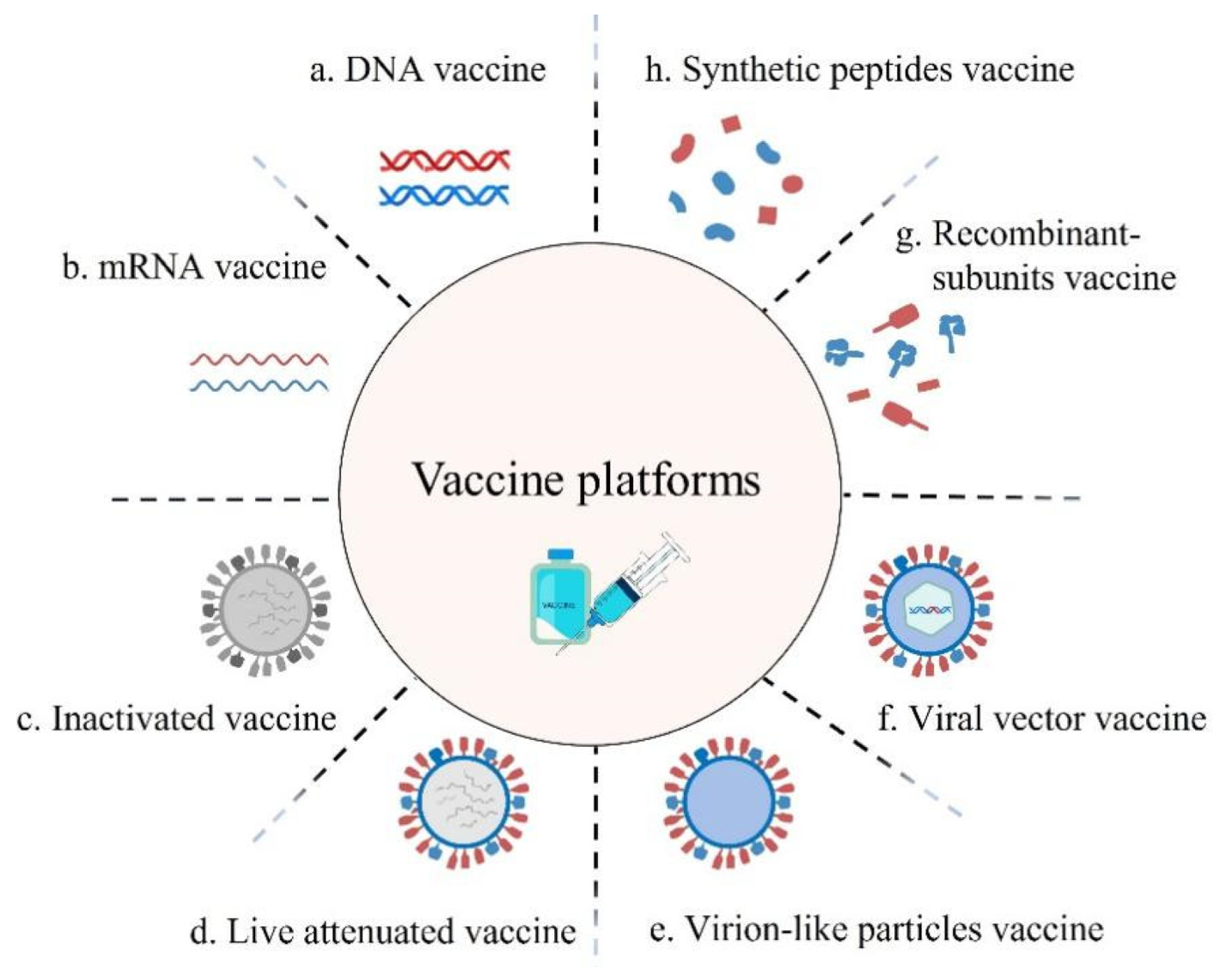
* Desarrollo de herramientas inmunoinformáticas que permitan analizar la respuesta inmune celular frente a diversos virus de interés sanitario y determinar la eficacia de sus vacunas a nivel de población mundial.

* Estudio de las respuestas inmunes celulares frente a enfermedades raras (artritis reactiva y síndrome del linfocito desnudo) y crónicas (espondiloartropatías).
* Inclusión de componentes del sistema inmune en la fabricación de tejidos humanos, especialmente piel, para uso clínico, farmacéutico y cosmético.
- * Generación de virus recombinantes como vectores vacunales.
Publicaciones destacadas
López, D., A. Barriga, E. Lorente, and C. Mir. 2019. Immunoproteomic Lessons for Human Respiratory Syncytial Virus Vaccine Design. J.Clin.Med. 8.
López, D., A. Barriga, E. Lorente, and C. Mir. 2019. Immunoproteomic Lessons for Human Respiratory Syncytial Virus Vaccine Design. J.Clin.Med. 8.
PUBMED DOILorente, E., A. Barriga, E. Barnea, C. Palomo, J. Garcia-Arriaza, C. Mir, M. Esteban, A. Admon, and D. López. 2019. Immunoproteomic analysis of a Chikungunya poxvirus-based vaccine reveals high HLA class II immunoprevalence. PLoS.Negl.Trop.Dis. 13:e0007547.
Lorente, E., A. Barriga, E. Barnea, C. Palomo, J. Garcia-Arriaza, C. Mir, M. Esteban, A. Admon, and D. López. 2019. Immunoproteomic analysis of a Chikungunya poxvirus-based vaccine reveals high HLA class II immunoprevalence. PLoS.Negl.Trop.Dis. 13:e0007547.
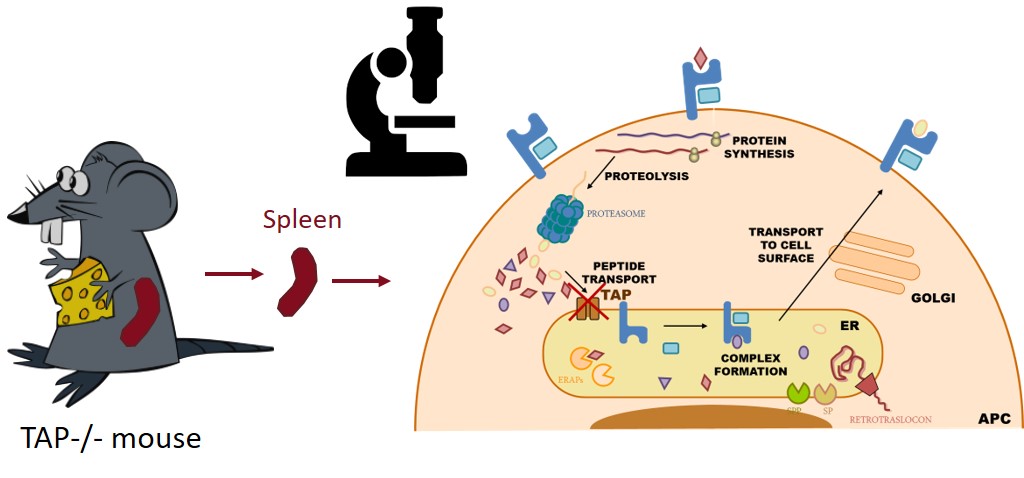
PUBMED DOIComputational characterization of the peptidome in transporter associated with antigen processing (TAP)-deficient cells.
Martin-Galiano, A. J. and Lopez, D. (2019) Computational characterization of the peptidome in transporter associated with antigen processing (TAP)-deficient cells. PLoS.ONE. 14, e0210583.
PUBMED DOIProteomics analysis reveals that structural proteins of the virion core and involved in gene expression are the main source for HLA class II ligands in vaccinia virus-infected cells.
Lorente, E., Martin-Galiano, A. J., Barnea, E., Barriga, A., Palomo, C., Garcia-Arriaza, J., Mir, C., Lauzurica, P., Esteban, M., Admon, A., and Lopez, D. (2019) Proteomics analysis reveals that structural proteins of the virion core and involved in gene expression are the main source for HLA class II ligands in vaccinia virus-infected cells. J.Proteome.Res. 18(9):3512-3520
PUBMED DOIGuasp, P., E. Lorente, A. Martín-Esteban, E. Barnea, P. Romania, D. Fruci, J. J. W. Kuiper, A. Admon, and J. A. López de Castro. 2019. Redundancy and Complementarity between ERAP1 and ERAP2 Revealed by their Effects on the Behcet's Disease-Associated HLA-B*51 Peptidome. Mol.Cell Proteomics.
Guasp, P., E. Lorente, A. Martín-Esteban, E. Barnea, P. Romania, D. Fruci, J. J. W. Kuiper, A. Admon, and J. A. López de Castro. 2019. Redundancy and Complementarity between ERAP1 and ERAP2 Revealed by their Effects on the Behcet's Disease-Associated HLA-B*51 Peptidome. Mol.Cell Proteomics.
PUBMED DOIFontela, M. G., L. Notario, E. Alari-Pahissa, E. Lorente, and P. Lauzurica. 2019
Fontela, M. G., L. Notario, E. Alari-Pahissa, E. Lorente, and P. Lauzurica. 2019. The Conserved Non-Coding Sequence 2 (CNS2) Enhances CD69 Transcription through Cooperation between the Transcription Factors Oct1 and RUNX1. Genes (Basel) 10.
PUBMED DOIInformación adicional
• Taxonomic study. Objective: Association of already described species to new clinical processes. Description of new bacterial species.
• Sensitivity studies against new antituberculous drugs: Objective: To evaluate the antimicrobial activity of new compounds for human use in clinical strains of Mycobacterium tuberculosis and in other species of non-tuberculous mycobacteria, for subsequent application in the treatment of these infections.
• Molecular epidemiology of tuberculosis. Objectives: Molecular characterization of the members of the M. tuberculosis complex. Transmission studies with special surveillance of MDR/XDR tuberculosis.
• Development of new methods of identification and detection of resistance in mycobacteria. Objectives: Optimization and development of molecular techniques for the diagnosis and detection of resistance.