Bacterial Genetics
Research Lines
Content with Investigacion .
Inmunología Microbiana e Inmunogenética
1. Análisis de la respuesta innata de mamíferos en la infección por Leishmania.
2. Caracterización inmunoproteómica en :
a. Streptococcus suis
b. Lactococcus garviae
c. Mycobacterium spp
3. Desarrollo de inmunoensayos analíticos basados en anticuerpos monoclonales (AcM) para detectar y cuantificar antígenos de origen animal, vegetal y microbiano.
4. Desarrollo y caracterización de AcM frente a los componentes del sistema del Complemento. Aplicación diagnóstica.
5. Desarrollo de reactivos de referencia y diseño de inmunoensayos para la evaluación cualitativa y cuantitativa de toxinas clostridiales.
6. Oferta tecnológica de producción de AcM y policlonales frente a substancias de interés industrial y biomédico.
El grupo está interesado en el estudio de la respuesta inmune desde una perspectiva multidisciplinar que incluye aproximaciones bioquímicas, biotecnológicas, genómicas, inmunoinformáticas y proteómicas, que junto con el uso adicional de modelos in vivo se encaminan al diseño de estrategias terapéuticas frente a diversas enfermedades crónicas, infecciosas y raras que poseen un claro componente inmunológico en su etiología.
Las principales líneas de investigación que está desarrollando el grupo en la actualidad son:
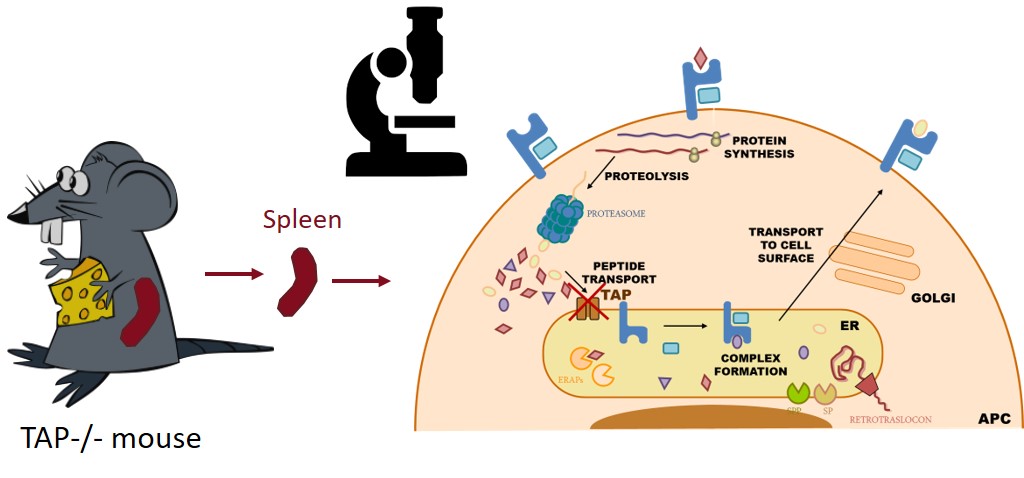
- * Análisis de las respuestas inmunes celulares frente a patógenos virales y bacterianos, mediante técnicas inmunoproteómicas, modelos in vivo con animales transgénicos y muestras humanas.
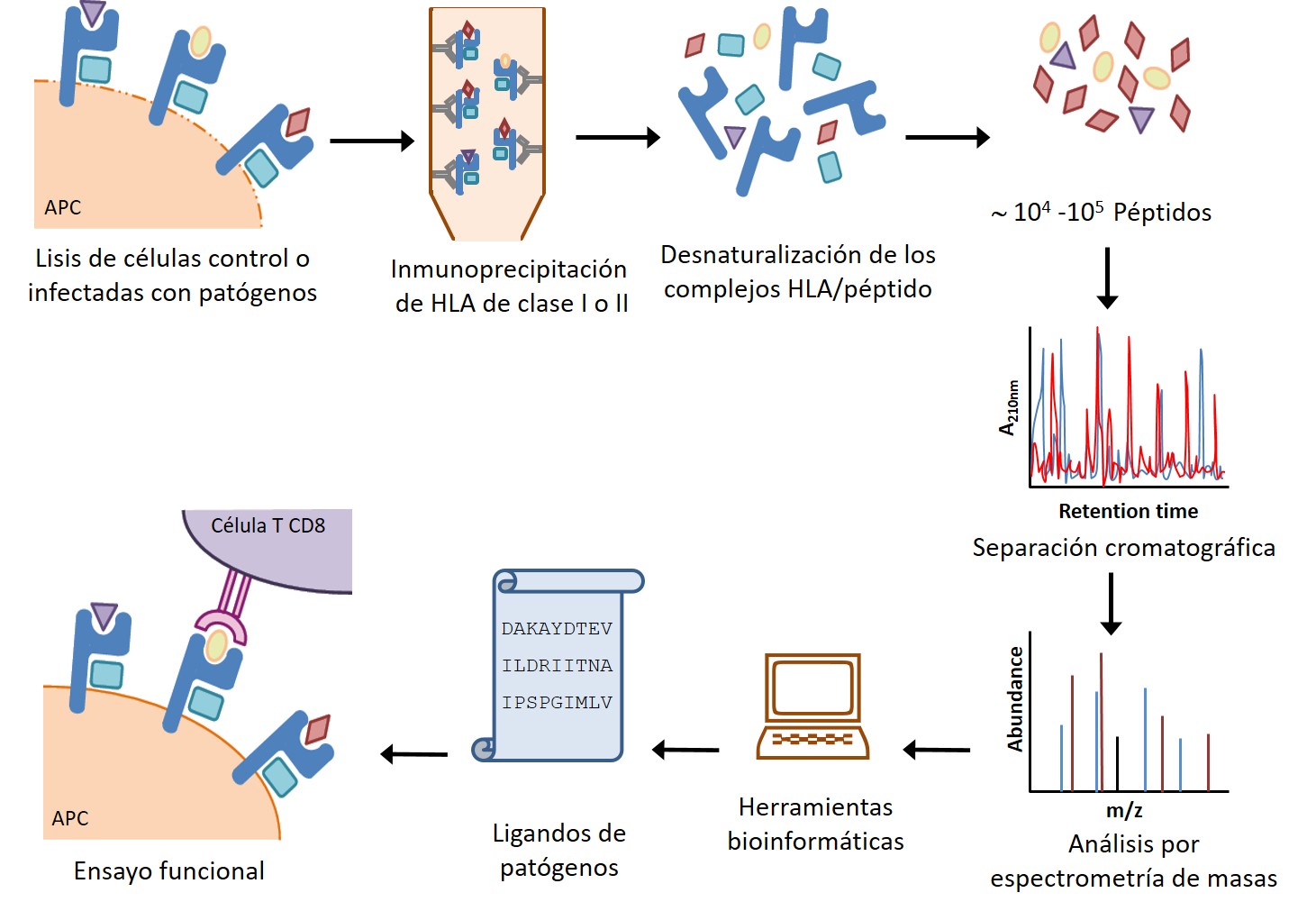
- * Caracterización de CD69: regulación génica, función reguladora inmune en homeostasis e infección y su uso como diana terapéutica, edición génica por CRISPR en modelos animales y celulares, etc.

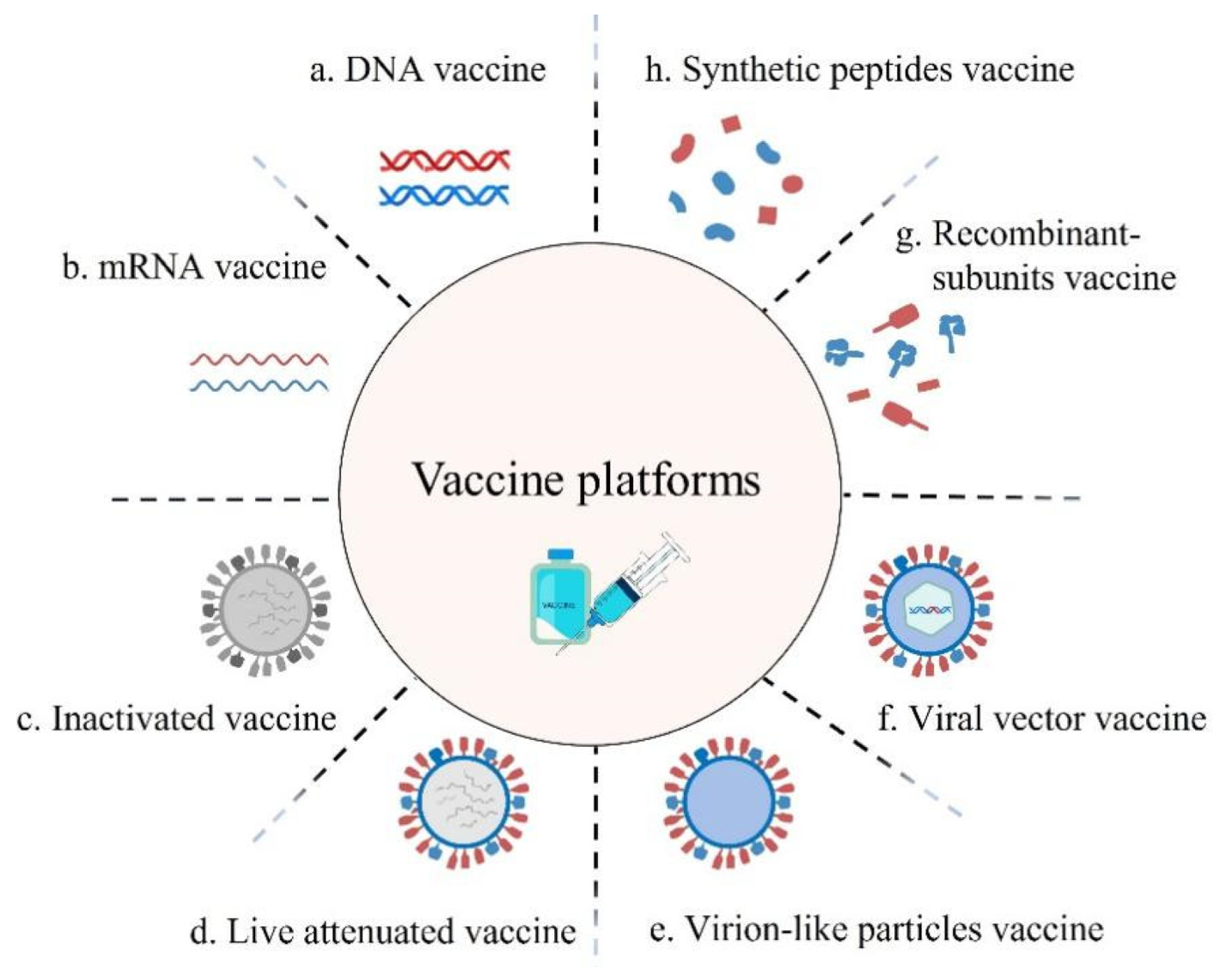
* Desarrollo de herramientas inmunoinformáticas que permitan analizar la respuesta inmune celular frente a diversos virus de interés sanitario y determinar la eficacia de sus vacunas a nivel de población mundial.

* Estudio de las respuestas inmunes celulares frente a enfermedades raras (artritis reactiva y síndrome del linfocito desnudo) y crónicas (espondiloartropatías).
* Inclusión de componentes del sistema inmune en la fabricación de tejidos humanos, especialmente piel, para uso clínico, farmacéutico y cosmético.
- * Generación de virus recombinantes como vectores vacunales.
Research projects
Content with Investigacion .
Los proyectos del grupo de los últimos años son los siguientes:
Proyecto “La interrelación de CD69 y el procesamiento antigénico en enfermedades infecciosas y autoinmunes" financiado por la Acción Estratégica en Salud del Ministerio de Ciencia, Innovación y Universidades. Año: 2023-2025.
Proyecto “Interacciones génicas y proteicas de CD69 y sus regiones génicas reguladoras con moléculas" financiado por la AEI. Año: 2022-2024.
Proyecto “Nuevas tecnologías de fabricación y optimización de tejidos: la piel como sistema modelo” financiado por el Programa de Actividades de I+D entre grupos de investigación de la Comunidad de Madrid en tecnologías 2018. Año: 2020-2023. Proyecto Coordinado por el Dr. Pablo Acedo de la Universidad Carlos III.
Proyecto “Estudio de CD69 como diana para mejorar el tratamiento de la leucopania y la movilización de células T de memoria de médula ósea" financiado por la Acción Estratégica en Salud del Ministerio de Ciencia, Innovación y Universidades. Año:2020-2024.
Proyecto “Diseño racional de una vacuna contra el virus respiratorio sincitial humano” financiado por la Acción Estratégica en Salud del Ministerio de Ciencia, Innovación y Universidades. Año: 2019-2022
Proyecto “Función de CD69 y sus elementos reguladores" financiado por la Acción Estratégica en Salud del Ministerio de Ciencia, Innovación y Universidades. Año: 2017-2022.
Proyecto “Diseño de vacunas recombinantes poliepitópicas para generar respuestas CD8+ contra virus emergentes” financiado por el Plan Nacional de I+D+i del Ministerio de Economía y Competitividad. Año: 2015-2017.
Proyecto “Análisis de los efectos de CD69 dependientes de S1P1 en modelos de infección e inflamación y estudio de su regulación” financiado por el FIS. Año: 2014-2017.
Proyecto “ADELVAC: Adenovirus con delecciones epitópicas para vacunación” financiado por el programa INNPACTO del Ministerio de Economía y Competitividad. Centro Nacional de Microbiología, Instituto de Salud Carlos III. Año: 2012-2014. Proyecto Coordinado por el Dr. Manel Cascallo de VCN BIOSCIENCES SL.
Proyecto “Diseño de vacunas multiepitópicas recombinantes para aumentar la respuesta inmune celular contra el VRSH” financiado por el Plan Nacional de I+D+i del Ministerio de Ciencia e Innovación. Año: 2012-2014.
Publications
Immunogenicity of a third dose with mRNA-vaccines in the ChAdOx1-S/BNT162b2 vaccination regimen against SARS-CoV-2 variants.
García-Pérez J, Borobia AM, Pérez-Olmeda M, Portolés A, Castaño L, Campins-Artí M, Bertrán MJ, Bermejo M, Arribas JR, López A, Ascaso-Del-Rio A, Arana-Arri E, Fuentes Camps I, Vilella A, Cascajero A, García-Morales MT, Castillo de la Osa M, Pérez Ingidua C, Lora D, Jiménez-Santana P, Pino-Rosa S, Gómez de la Cámara A, De La Torre-Tarazona E, Calonge E, Cruces R, Belda-Iniesta C, Alcamí J, Frías J, Carcas AJ, Díez-Fuertes F. iScience. 2024; 27(9):110728
PUBMED DOILonger intervals between SARS-CoV-2 infection and mRNA-1273 doses improve the neutralization of different variants of concern
García-Pérez J, Bermejo M, Ramírez-García A, De La Torre-Tarazona HE, Cascajero A, Castillo de la Osa M, Jiménez P, Aparicio Gómez M, Calonge E, Sancho-López A, Payares-Herrera C, Layunta Acero R, Vicente-Izquierdo L, Avendaño-Solá C, Alcamí J, Pérez-Olmeda M, Díez-Fuertes F. J Med Virol. 2023; 95(3):e28679
PUBMED DOIImmune response and reactogenicity after immunization with two-doses of an experimental COVID-19 vaccine (CVnCOV) followed by a third-fourth shot with a standard mRNA vaccine (BNT162b2): RescueVacs multicenter cohort study
Ascaso-Del-Rio A, García-Pérez J, Pérez-Olmeda M, Arana-Arri E, Vergara I, Pérez-Ingidua C, Bermejo M, Castillo de la Osa M, Imaz-Ayo N, Riaño Fernández I, Astasio González O, Díez-Fuertes F, Meijide S, Arrizabalaga J, Hernández Gutiérrez L, de la Torre-Tarazona HE, Mariano Lázaro A, Vargas-Castrillón E, Alcamí J, Portolés A; RescueVac study Group. EClinicalMedicine. 2022; 51:101542
PUBMED DOIImmunogenic dynamics and SARS-CoV-2 variant neutralisation of the heterologous ChAdOx1-S/BNT162b2 vaccination: Secondary analysis of the randomised CombiVacS study
García-Pérez J, González-Pérez M, Castillo de la Osa M, Borobia AM, Castaño L, Bertrán MJ, Campins M, Portolés A, Lora D, Bermejo M, Conde P, Hernández-Gutierrez L, Carcas A, Arana-Arri E, Tortajada M, Fuentes I, Ascaso A, García-Morales MT, Erick de la Torre-Tarazona H, Arribas JR, Imaz-Ayo N, Mellado-Pau E, Agustí A, Pérez-Ingidua C, Gómez de la Cámara A, Ochando J, Belda-Iniesta C, Frías J, Alcamí J, Pérez-Olmeda M; CombiVacS study Group. EClinicalMedicine. 2022; 50:101529
PUBMED DOITranscriptomic Evidence of the Immune Response Activation in Individuals With Limb Girdle Muscular Dystrophy Dominant 2 (LGMDD2) Contributes to Resistance to HIV-1 Infection
Diez-Fuertes F, López-Huertas MR, García-Pérez J, Calonge E, Bermejo M, Mateos E, Martí P, Muelas N, Vílchez JJ, Coiras M, Alcamí J, Rodríguez-Mora S. Front Cell Dev Biol. 2022; 10:839813
PUBMED DOIImmunogenicity and reactogenicity of BNT162b2 booster in ChAdOx1-S-primed participants (CombiVacS): a multicentre, open-label, randomised, controlled, phase 2 trial
Borobia AM, Carcas AJ, Pérez-Olmeda M, Castaño L, Bertran MJ, García-Pérez J, Campins M, Portolés A, González-Pérez M, García Morales MT, Arana-Arri E, Aldea M, Díez-Fuertes F, Fuentes I, Ascaso A, Lora D, Imaz-Ayo N, Barón-Mira LE, Agustí A, Pérez-Ingidua C, Gómez de la Cámara A, Arribas JR, Ochando J, Alcamí J, Belda-Iniesta C, Frías J; CombiVacS Study Group. Lancet. 2021; 398(10295):121-130
PUBMED DOIBroth microdilution protocol for determining antimicrobial susceptibility of Legionella pneumophila to clinically relevant antimicrobials
Sewell M, Farley C, Portal EAR, Lindsay D, Ricci ML, Jarraud S, Scaturro M, Descours G, Krøvel AV, Barton R, Boostom I, Ure R, Kese D, Gaia V, Golob M, Paukner S, Ginevra C, Afshar B, Nadarajah S, Wybo I, Michel C, Echahdi F, González-Rubio JM, González-Camacho F, Mentasti M, Flountzi AS, Petzold M, Moran-Gilad J, Uldum S, Winchell J, Wooton M, Bernard K, Jones LC, Chalker VJ, Spiller OB. J Microbiol Methods. 2025 Jan;228:107071.
PUBMED DOIEpidemiology, molecular characterisation and antimicrobial susceptibility of Neisseria gonorrhoeae isolates in Madrid, Spain, in 2016
María D. Guerrero-Torres, María B. Menéndez, Carmen S. Guerras, Estela Tello, Juan Ballesteros, Petunia Clavo, Teresa Puerta, Mar Vera, Oskar Ayerdi, Juan C. Carrio, Inmaculada Monzo, Jorge del Romero, Julio A. Vázquez, Raquel Abad. 20. María D. Guerrero-Torres, María B. Menéndez, Carmen S. Guerras, Estela Tello, Juan Ballesteros, Petunia Clavo, Teresa Puerta, Mar Vera, Oskar Ayerdi, Juan C. Carrio, Inmaculada Monzo, Jorge del Romero, Julio A. Vázquez, Raquel Abad. Epidemiol Infect. 2019 Sep 24;147:e274
PUBMED DOIThe global meningitis genome partnership
Rodgers E, Bentley SD, Borrow R, Bratcher HB, Brisse S, Brueggemann AB, Caugant DA, Findlow J, Fox L, Glennie L, Harrison LH, Harrison OB, Heyderman RS, van Rensburg MJ, Jolley KA, Kwambana-Adams B, Ladhani S, LaForce M, Levin M, Lucidarme J, MacAlasdair N, Maclennan J, Maiden MCJ, Maynard-Smith L, Muzzi A, Oster P, Rodrigues CMC, Ronveaux O, Serino L, Smith V, van der Ende A, Vázquez J, Wang X, Yezli S, Stuart JM. J Infect. 2020; 81(4): 510-520
PUBMED DOIThe importance of microbiology reference laboratories and adequate funding for infectious disease surveillance
Shaw D, Torreblanca RA, Amin-Chowdhury Z, Bautista A, Bennett D, Broughton K, Casanova C, Choi EH, Claus H, Corcoran M, Cottrell S, Cunney R, Cuypers L, Dalby T, Davies H, de Gouveia L, Deghmane AE, Desmet S, Domenech M, Drew R, Plessis MD, Duarte C, Fuursted K, Golden A, Almeida SCG, Henares D, Henriques-Normark B, Hilty M, Hoffmann S, Humphreys H, Jacobsson S, Johnson C, Jolley KA, Kawabata A, Kozakova J, Kristinsson KG, Krizova P, Kuch A, Ladhani S, Lâm TT, Ayala MEL, Lindholm L, Litt D, Maiden MCJ, Martin I, Martiny D, Mattheus W, McCarthy ND, Meehan M, Meiring S, Mölling P, Morfeldt E, Morgan J, Mulhall R, Muñoz-Almagro C, Murdoch D, Musilek M, Novakova L, Oftadeh S, Perez-Arguello A, Pérez-Vázquez MD, Perrin M, Prevost B, Roberts M, Rokney A, Ron M, Sanabria OM, Scott KJ, Sempere J, Siira L, de Lemos APS, Sintchenko V, Skoczyńska A, Slotved HC, Smith AJ, Taha MK, Toropainen M, Tzanakaki G, Vainio A, van der Linden MPG, van Sorge NM, Varon E, Moreno JV, Vohrnova S, von Gottberg A, Yuste J, Brueggemann AB. Lancet Digit Health. 2025 Apr;7(4):e275-e281.
PUBMED DOIAntimicrobial resistance and epidemiological aspects of Neisseria gonorrhoeae in the province of Lleida, Spain (2017-2024).
Cumplido A, Aramburu J, Font M, Montes M, Abad R, López E, Bernet A, Mormeneo S, Prats I, García M, Sánchez E, Bellés A. Enferm Infecc Microbiol Clin (Engl Ed). 2025 Mar;43(3):156-161.
PUBMED DOIExploring the sequence diversity and surface expression of Factor H-Binding Protein among invasive serogroup B meningococcal strains from selected European countries
Clark SA, Willerton L, Claus H, Carannante A, Stefanelli P, Abad R, Vázquez JA, Borrow R. Hum Vaccin Immunother. 2024 Dec 31;20(1):2427471
PUBMED DOIResultado falso negativo en diversas PCR multiplex y monoplex en un episodio de bacteriemia por Neisseria meningitidis. Implicaciones diagnósticas, terapéuticas y epidemiológicas [False negative result in both multiplex and monoplex PCR in a case of Neisseria meningitidis bacteremia. Diagnostic, therapeutic and epidemiological implications]
Monforte ML, Cebollada R, Escobar MJ, Abad R, Aspiroz C. Rev Esp Quimioter. 2024 Oct;37(5):427-428
PUBMED DOIGlobal Meningococcal Initiative: Insights on antibiotic resistance, control strategies and advocacy efforts in Western Europe
Borrow R, Campbell H, Caugant DA, Cherkaoui A, Claus H, Deghmane AE, Dinleyici EC, Harrison LH, Hausdorff WP, Bajanca-Lavado P, Levy C, Mattheus W, Mikula-Pratschke C, Mölling P, Sáfadi MA, Smith V, van Sorge NM, Stefanelli P, Taha MK, Toropainen M, Tzanakaki G, Vázquez J. . J Infect. 2024; 89(6): 106335
PUBMED DOIMeningococcal disease in the Middle East: A report from the Global Meningococcal Initiative
Al-Abri SS, Abuhasan MY, Albayat SSA, Bai X, Bastaki H, Borrow R, Caugant DA, Dbaibo G, Deghmane AE, Dinleyici EC, Ghuneim N, Sheek-Hussein M, Lucidarme J, Leng S, Koliou MG, Sáfadi MAP, Salman JA, Al-Sanouri T, Smith V, Taha MK, Vázquez J, Wright C, Yezli S. J Infect. 2024; 88(2):71-76.
PUBMED DOIAntimicrobial-resistant Neisseria gonorrhoeae in Europe in 2020 compared with in 2013 and 2018: a retrospective genomic surveillance study.
Golparian D, Cole MJ, Sánchez-Busó L, Day M, Jacobsson S, Uthayakumaran T, Abad R, Bercot B, Caugant DA, Heuer D, Jansen K, Pleininger S, Stefanelli P, Aanensen DM, Bluemel B, Unemo M; Euro-GASP study group. Lancet Microbe. 2024 May;5(5):e478-e488.
PUBMED DOIAdditional Information
Streptococcus pneumoniae is a human pathogen that, despite the development of vaccines, continues to be an important cause of mortality and morbidity. We investigate the mechanisms of antibiotic resistance in this bacterium. On the one hand by identifying new therapeutic targets and on the other hand by investigating the molecular basis of the action of antibiotics already used in clinical practice (the fluoroquinolones levofloxacin and moxifloxacin) or not yet used (seconeolitsine). For this purpose, we used a multidisciplinary analysis involving genomics, transcriptomics and proteomics to understand the organization of the S. pneumoniae chromosome and the identification of the factors that stabilize this organization, including ncRNAs. Changes in the level of global supercoiling, either by inhibition of gyrase (decrease) or by inhibition of topoisomerase I (increase) alter the transcriptome. The modulated genes are located in domains, whose genes show specific functional characteristics. The aim is to identify new factors essential for S. pneumoniae physiology and to characterize transcriptional regulation in response to topological stress. In addition, RNA interference technology and CRISPR systems will be used as novel antibacterials. These studies will establish the bases for translational research aimed at the development of new therapeutic targets for the treatment of pneumococcal diseases.
Streptococcus pneumoniae is a human pathogen that, despite the development of vaccines, continues to be an important cause of mortality and morbidity. We investigate the mechanisms of antibiotic resistance in this bacterium. On the one hand by identifying new therapeutic targets and on the other hand by investigating the molecular basis of the action of antibiotics already used in clinical practice (the fluoroquinolones levofloxacin and moxifloxacin) or not yet used (seconeolitsine). For this purpose, we used a multidisciplinary analysis involving genomics, transcriptomics and proteomics to understand the organization of the S. pneumoniae chromosome and the identification of the factors that stabilize this organization, including ncRNAs. Changes in the level of global supercoiling, either by inhibition of gyrase (decrease) or by inhibition of topoisomerase I (increase) alter the transcriptome. The modulated genes are located in domains, whose genes show specific functional characteristics. The aim is to identify new factors essential for S. pneumoniae physiology and to characterize transcriptional regulation in response to topological stress. In addition, RNA interference technology and CRISPR systems will be used as novel antibacterials. These studies will establish the bases for translational research aimed at the development of new therapeutic targets for the treatment of pneumococcal diseases.