Viral Biology
Research Lines
Content with Investigacion .
Inmunología Microbiana e Inmunogenética
1. Análisis de la respuesta innata de mamíferos en la infección por Leishmania.
2. Caracterización inmunoproteómica en :
a. Streptococcus suis
b. Lactococcus garviae
c. Mycobacterium spp
3. Desarrollo de inmunoensayos analíticos basados en anticuerpos monoclonales (AcM) para detectar y cuantificar antígenos de origen animal, vegetal y microbiano.
4. Desarrollo y caracterización de AcM frente a los componentes del sistema del Complemento. Aplicación diagnóstica.
5. Desarrollo de reactivos de referencia y diseño de inmunoensayos para la evaluación cualitativa y cuantitativa de toxinas clostridiales.
6. Oferta tecnológica de producción de AcM y policlonales frente a substancias de interés industrial y biomédico.
El grupo está interesado en el estudio de la respuesta inmune desde una perspectiva multidisciplinar que incluye aproximaciones bioquímicas, biotecnológicas, genómicas, inmunoinformáticas y proteómicas, que junto con el uso adicional de modelos in vivo se encaminan al diseño de estrategias terapéuticas frente a diversas enfermedades crónicas, infecciosas y raras que poseen un claro componente inmunológico en su etiología.
Las principales líneas de investigación que está desarrollando el grupo en la actualidad son:
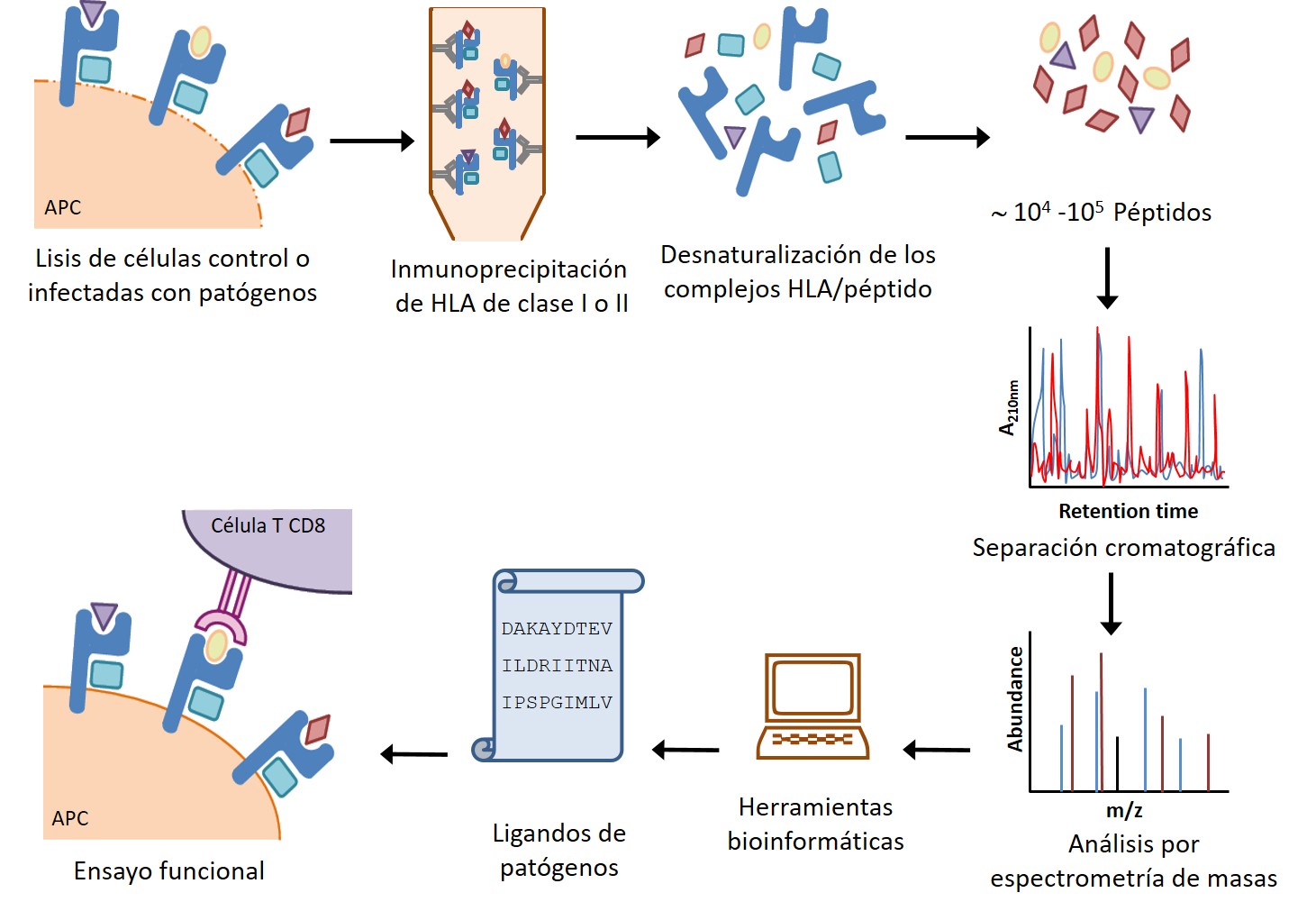
- * Análisis de las respuestas inmunes celulares frente a patógenos virales y bacterianos, mediante técnicas inmunoproteómicas, modelos in vivo con animales transgénicos y muestras humanas.
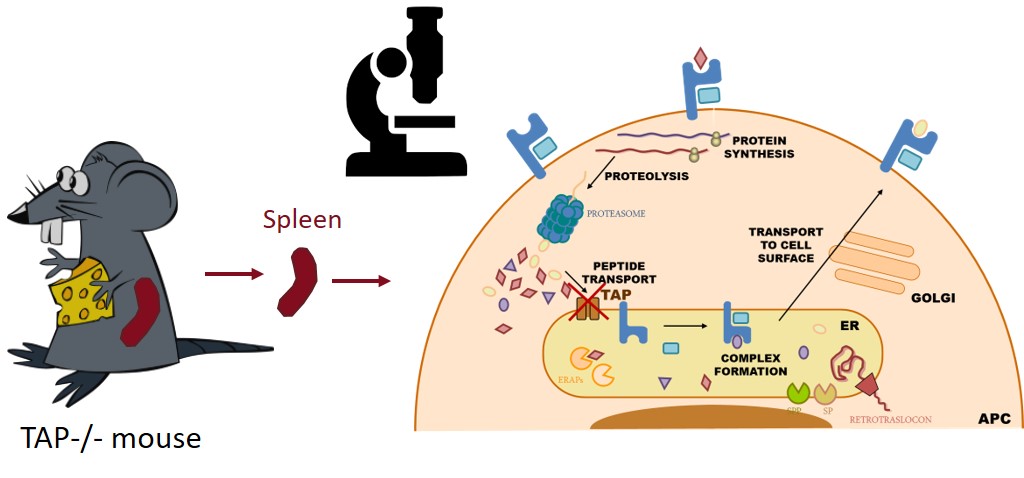
- * Caracterización de CD69: regulación génica, función reguladora inmune en homeostasis e infección y su uso como diana terapéutica, edición génica por CRISPR en modelos animales y celulares, etc.

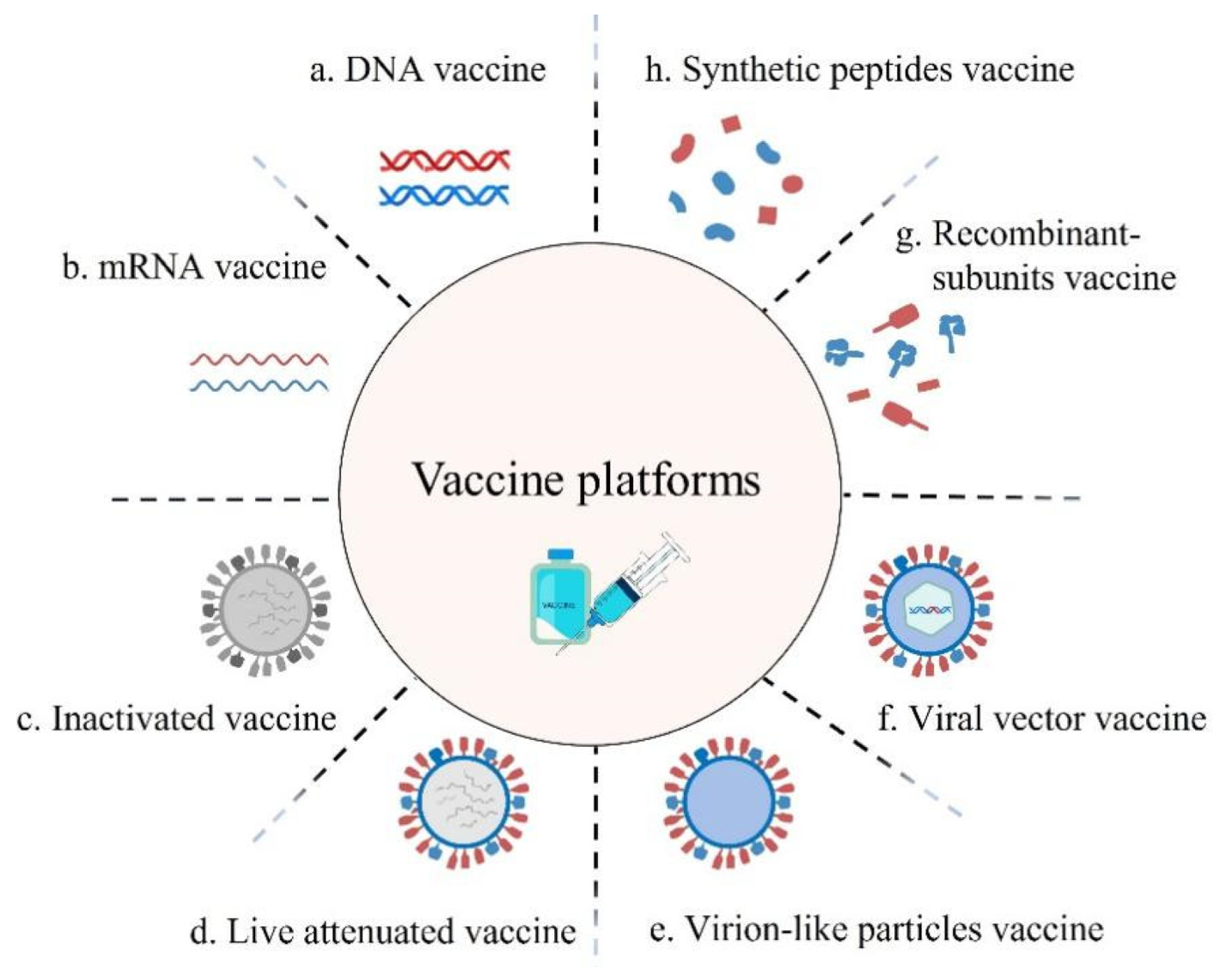
* Desarrollo de herramientas inmunoinformáticas que permitan analizar la respuesta inmune celular frente a diversos virus de interés sanitario y determinar la eficacia de sus vacunas a nivel de población mundial.

* Estudio de las respuestas inmunes celulares frente a enfermedades raras (artritis reactiva y síndrome del linfocito desnudo) y crónicas (espondiloartropatías).
* Inclusión de componentes del sistema inmune en la fabricación de tejidos humanos, especialmente piel, para uso clínico, farmacéutico y cosmético.
- * Generación de virus recombinantes como vectores vacunales.
Research projects
Content with Investigacion .
Los proyectos del grupo de los últimos años son los siguientes:
Proyecto “La interrelación de CD69 y el procesamiento antigénico en enfermedades infecciosas y autoinmunes" financiado por la Acción Estratégica en Salud del Ministerio de Ciencia, Innovación y Universidades. Año: 2023-2025.
Proyecto “Interacciones génicas y proteicas de CD69 y sus regiones génicas reguladoras con moléculas" financiado por la AEI. Año: 2022-2024.
Proyecto “Nuevas tecnologías de fabricación y optimización de tejidos: la piel como sistema modelo” financiado por el Programa de Actividades de I+D entre grupos de investigación de la Comunidad de Madrid en tecnologías 2018. Año: 2020-2023. Proyecto Coordinado por el Dr. Pablo Acedo de la Universidad Carlos III.
Proyecto “Estudio de CD69 como diana para mejorar el tratamiento de la leucopania y la movilización de células T de memoria de médula ósea" financiado por la Acción Estratégica en Salud del Ministerio de Ciencia, Innovación y Universidades. Año:2020-2024.
Proyecto “Diseño racional de una vacuna contra el virus respiratorio sincitial humano” financiado por la Acción Estratégica en Salud del Ministerio de Ciencia, Innovación y Universidades. Año: 2019-2022
Proyecto “Función de CD69 y sus elementos reguladores" financiado por la Acción Estratégica en Salud del Ministerio de Ciencia, Innovación y Universidades. Año: 2017-2022.
Proyecto “Diseño de vacunas recombinantes poliepitópicas para generar respuestas CD8+ contra virus emergentes” financiado por el Plan Nacional de I+D+i del Ministerio de Economía y Competitividad. Año: 2015-2017.
Proyecto “Análisis de los efectos de CD69 dependientes de S1P1 en modelos de infección e inflamación y estudio de su regulación” financiado por el FIS. Año: 2014-2017.
Proyecto “ADELVAC: Adenovirus con delecciones epitópicas para vacunación” financiado por el programa INNPACTO del Ministerio de Economía y Competitividad. Centro Nacional de Microbiología, Instituto de Salud Carlos III. Año: 2012-2014. Proyecto Coordinado por el Dr. Manel Cascallo de VCN BIOSCIENCES SL.
Proyecto “Diseño de vacunas multiepitópicas recombinantes para aumentar la respuesta inmune celular contra el VRSH” financiado por el Plan Nacional de I+D+i del Ministerio de Ciencia e Innovación. Año: 2012-2014.
Publications
Pediatric drug-resistant tuberculosis in Madrid family matters
7. Santiago B, Baquero-Artiago F, Mejias A, Blázquez D, Jimenez MS, Mellado-Peña MJ, EREMITA Study group. Pediatric drug-resistant tuberculosis in Madrid: family matters. The Pediatric Infectious Disease Journal. 2014; 33:345-350.
PUBMED DOIMycobacterium kumamotonense, another Member of the Mycobacterium terrae Complex Unusually Carrying Two Copies of the Ribosomal RNA Operon
8. Menéndez MC, Jiménez MS, Yubero J, García MJ. Mycobacterium kumamotonense, another Member of the Mycobacterium terrae Complex Unusually Carrying Two Copies of the Ribosomal RNA Operon. Mycobac Dis; 2014; 4:176.
DOIMycobacterium mageritense meningitis in an immunocompetent patient with an intrathecal catheter.
9. Muñoz-Sanz A, Rodríguez Vidigal FF, Vera-Tome A, Jimenez MS. Mycobacterium mageritense meningitis in an immunocompetent patient with an intrathecal catheter. Enfer Infecc Microbiol Clin. 2013; 31:59-6
PUBMED DOIMeasles virus genotype D4 strains with non-standard length M-F non-coding region circulated during the major outbreaks of 2011-2012 in Spain.
2. Gil H, Fernández-García A*, Mosquera MM, Hübschen JM, Castellanos AM, de Ory F, Masa-Calles J, Echevarría JE.Measles virus genotype D4 strains with non-standard length M-F non-coding region circulated during the major outbreaks of 2011-2012 in Spain. PLoS One. 2018 Jul. 16;13(7):e0199975. * Corresponding author.
PUBMED DOIIsolation, antigenicity and immunogenicity of Lleida Bat Lyssavirus
3. Banyard AC, Selden D, Wu G; Thorne L, Jennings D, Marston D, Finke S, Freuling CM, Mueller T, Echevarria JE, Fooks AR. Isolation, antigenicity and immunogenicity of Lleida Bat Lyssavirus. Journal of General Virology, 2018. 99(12):1590-1599
PUBMED DOIShift within age-groups of mumps incidence, hospitalizations and severe complications in a highly vaccinated population
6. López-Perea N, Masa-Callesa J, Torres de Miera MV, Fernández-García A, Echevarría JE, de Ory F, Martínez de Aragón MV. Shift within age-groups of mumps incidence, hospitalizations and severe complications in a highly vaccinated population. Spain, 1998–2014. Vaccine, 2017, 35(34): 4339-4345.
PUBMED DOIThe Complexity of Antibody Responses Elicited against the Respiratory Syncytial Virus Glycoproteins in Hospitalized Children Younger than 2 Years
2. Trento A, Rodriguez-Fernandez R, Gonzalez-Sanchez MI, Gonzalez-Martinez F, Mas V, Vazquez M, et al. The Complexity of Antibody Responses Elicited against the Respiratory Syncytial Virus Glycoproteins in Hospitalized Children Younger than 2 Years. Front Microbiol. 2017;8:2301.
PUBMED DOIPotent single-domain antibodies that arrest respiratory syncytial virus fusion protein in its prefusion state.
3. Rossey I, Gilman MS, Kabeche SC, Sedeyn K, Wrapp D, Kanekiyo M, et al. Potent single-domain antibodies that arrest respiratory syncytial virus fusion protein in its prefusion state. Nat Commun. 2017;8:14158.
PUBMED DOIRapid profiling of RSV antibody repertoires from the memory B cells of naturally infected adult donors
6. Gilman MS, Castellanos CA, Chen M, Ngwuta JO, Goodwin E, Moin SM, et al. Rapid profiling of RSV antibody repertoires from the memory B cells of naturally infected adult donors. Sci Immunol. 2016;1(6).
PUBMED DOICharacterization of a Prefusion-Specific Antibody That Recognizes a Quaternary, Cleavage-Dependent Epitope on the RSV Fusion Glycoprotein.
8. Gilman MS, Moin SM, Mas V, Chen M, Patel NK, Kramer K, et al. Characterization of a Prefusion-Specific Antibody That Recognizes a Quaternary, Cleavage-Dependent Epitope on the RSV Fusion Glycoprotein. PLoS Pathog. 2015;11(7):e1005035.
PUBMED DOIPolyclonal and monoclonal antibodies specific for the six-helix bundle of the human respiratory syncytial virus fusion glycoprotein as probes of the protein post-fusion conformation.
9. Palomo C, Mas V, Vazquez M, Cano O, Luque D, Terron MC, et al. Polyclonal and monoclonal antibodies specific for the six-helix bundle of the human respiratory syncytial virus fusion glycoprotein as probes of the protein post-fusion conformation. Virology. 2014;460-461:119-27.
PUBMED DOIBiophysical properties of single rotavirus particles account for the functions of protein shells in a multilayered virus
Jiménez-Zaragoza M., Yubero M.L., Martín-Forero E., Castón J.R., Reguera D., Luque D.*, de Pablo P.J., Rodríguez J.M. 2018. Biophysical properties of single rotavirus particles account for the functions of protein shells in a multilayered virus. eLife 7: e37295. *Corresponding author.
PUBMED DOIAcquisition of functions on the outer capsid surface during evolution of double-stranded RNA fungal viruses
Mata C.P., Luque D., Gómez-Blanco J., Rodríguez J.M., González J.M., Suzuki N., Ghabrial S.A., Carrascosa J.L., Trus B.L., Castón J.R. 2017. Acquisition of functions on the outer capsid surface during evolution of double-stranded RNA fungal viruses. PLoS Pathog. 13(12):e1006755.
PUBMED DOIStructural Insights into the Assembly and Regulation of Distinct Viral Capsid Complexes
Sarker S., C. Terrón M., Khandokar Y., Aragão D., Hardy J.M., Radjainia M., Jiménez-Zaragoza M., de Pablo P.J., Coulibaly F., Luque D., Raidal D.R., Forwood J.K. 2016. Structural Insights into the Assembly and Regulation of Distinct Viral Capsid Complexes. Nat. Commun. 7:13014. IF: 12.124; D1.
PUBMED DOIHeterodimers as the structural unit of the T=1 capsid of the fungal dsRNA Rosellinia necatrix quadrivirus 1
Luque D., Mata C.P., González-Camacho F., González J.M., Gómez-Blanco J., Alfonso C., Rivas G., Havens W.M., Kanematsu S., Suzuki N., Ghabrial S.A., Trus B.L., Castón J.R. 2016. Heterodimers as the structural unit of the T=1 capsid of the fungal dsRNA Rosellinia necatrix quadrivirus 1. J Virol. 90(24):11220-11230. IF: 4.666, Q1.
PUBMED DOISelf-assembly and characterization of small and monodisperse dye nanospheres in a protein cage
Luque D., de la Escosura A., Snijder J., Brasch M., Burnley R.J, Koay M.S.T., Carrascosa J.L., Wuite G.J.L., Roos W.H., Heck A.J.R., J.J.L.M Cornelissen, Torres T., Castón J.R. 2014. Self-assembly and characterization of small and monodisperse dye nanospheres in a protein cage. Chem. Sci.,5, 575-581. IF: 9.211, D1.
DOIAdditional Information
The research activity of the Viral Biology group since its beginnings in the 1980s has focused on respiratory viruses, especially on the study of the mechanisms of virus entry into the cell, evolutionary aspects, antigenic properties and vaccine development.
Currently, the group's objectives are focused on the characterisation of the immune response and the development of vaccines against human pneumoviruses: human respiratory syncytial virus (hRSV) and human metapneumovirus (hMPV).
Both viruses are considered to be important respiratory pathogens of high clinical relevance, especially in the paediatric population.
Safe and effective vaccines against these viruses are currently not available. Soluble protein subunits based on the fusion protein (F-protein) of hRSV and hMPV are being developed in the laboratory by protein engineering for use as vaccines against human pneumoviruses.
On the other hand, and thanks to the characterisation of the type of humoral response induced by the F proteins of these viruses, the laboratory is also involved in the isolation of monoclonal antibodies and nanoantibodies for use as treatments against these viruses.
The research activity of the Viral Biology group since its beginnings in the 1980s has focused on respiratory viruses, especially on the study of the mechanisms of virus entry into the cell, evolutionary aspects, antigenic properties and vaccine development.
Currently, the group's objectives are focused on the characterisation of the immune response and the development of vaccines against human pneumoviruses: human respiratory syncytial virus (hRSV) and human metapneumovirus (hMPV).
Both viruses are considered to be important respiratory pathogens of high clinical relevance, especially in the paediatric population.
Safe and effective vaccines against these viruses are currently not available. Soluble protein subunits based on the fusion protein (F-protein) of hRSV and hMPV are being developed in the laboratory by protein engineering for use as vaccines against human pneumoviruses.
On the other hand, and thanks to the characterisation of the type of humoral response induced by the F proteins of these viruses, the laboratory is also involved in the isolation of monoclonal antibodies and nanoantibodies for use as treatments against these viruses.
The current director of CNM is Dr. José Miguel Rubio Muñoz.
Dr. José Miguel Rubio has a degree in Biological Sciences from the Universidad Autónoma de Madrid (1986) and a PhD in Biological Sciences from the same university (1992). He carried out his doctoral thesis at the Department of Genetics of the Universidad Autónoma de Madrid, as Associate Professor (1988-1989), and at the School of Biology of the University of East Anglia in Norwich, UK, as Senior Research Assistant (1989-1992).
During his postdoctoral period he obtained a grant from the European Commission within the Human Capital and Mobility Program to be carried out at the University of “La Sapienza” in Rome, Italy and the Institute of Molecular Biology and Biotechnology in Crete, Greece (1993-1994). Subsequently, he made a further stay funded by the WHO and the university itself at the Department of Entomology, Wageningen University, The Netherlands (1994-1996).
Since 1997 he has been a member of the Instituto de Salud Carlos III (ISCIII), where he joined the Department of Parasitology of the National Center of Microbiology, as an EU-INCO postdoctoral fellow and later with a grant from the Autonomous Community of Madrid (CAM). She was part of the founding group of the National Center for Tropical Medicine (2003-2006) and of the 24/7 Alerts and Emergencies Unit (2006-2018) and is currently Head of the Malaria and Emerging Parasitosis Unit of the National Microbiology Center and is part, as research staff, of the Center for Biomedical Research Network on Infectious Diseases (CIBERINFEC/ISCIII).
During his scientific career he has been Visiting Scientist at the Leonidas e Marie Dean Center (FIOCRUZ-AMAZONAS, Manaus, Brazil) and is an External Consultant of the Parasitology Departments of Cairo University (Egypt) and the Medical Research Center (MRC) of Kuala Lumpur (Malaysia). He also belongs or has belonged to different national and international committees: Member of the expert group for malaria control of the European Centre for Disease Control (ECDC) since 2011; Expert-Evaluator for health programs of the European Commission since 2004; Spanish Representative (commissioned by ISCIII and MSC) in the Technical Scientific Committee of the TDR (WHO) 2007-2008; Spanish Deputy Focal Point for microbiology at the European Centre for Disease Control (ECDC) from 2012 to 2020; and, member of the Research Ethics Committee of ISCIII until 2019.
In this period he has published more than 100 articles in international indexed journals, 10 book chapters and has been co-editor of two books in the area of malaria, tropical medicine and neglected diseases. He has participated in 58 competitively funded research projects, 20 of them international, having been the principal investigator in 8 national and 11 international projects as PI of the project or WP leader. In addition, he has led five agreements with companies. Currently he has been awarded four sexenios of research, being presented this year 2025 to the fifth. In the teaching field, he participates in different postgraduate programs in the areas of microbiology and parasitology, having directed seven doctoral theses and more than 20 Master's or Degree final projects, both nationally and internationally.
El laboratorio de Referencia e Investigación en Resistencia a Antibióticos ofrece una amplia cartera de servicios al Sistema Nacional de Salud, las cuales pueden solicitarse en cnm-laboratorios.isciii.es. Jefe del Laboratorio: Jesús Oteo Iglesias (Punto focal Nacional de Resistencia antibiótica).
Dispone de dos programas de Vigilancia oficiales y gratuitos que engloban los ensayos ofertados ya sea como aislamientos individuales o mediante estudio de brotes. El Laboratorio utiliza asimismo técnicas de PCR en tiempo real para la detección de genes de resistencia, estas técnicas se han adaptado a un formato multiplex que permite detectar varios genes en la misma reacción. En los últimos años se han incluido metodologías basadas en la secuenciación de genomas completos para el análisis de bacterias multiresistentes (WGS).
Programa de vigilancia de Haemophilus influenzae. Responsables: María Pérez Vázquez (Punto focal Nacional de Haemophilus influenzae) y Belén Aracil. Laboratorio encargado de la identificación, estudio de sensibilidad y análisis genotípico de aislados de Haemophilus influenzae, centrándose esencialmente en la patología invasiva debida este patógeno.
Programa de vigilancia de Resistencia a Antibióticos. Responsables: María Pérez Vázquez y Belén Aracil (Punto focal Nacional de Resistencia antibiótica). Laboratorio encargado de la identificación, el estudio de sensibilidad antibiótica, y el diagnóstico fenotípico y genotípico de los diferentes mecanismos de resistencia a antibióticos fundamentalmente en enterobacterias y gram-negativos no fermentadores y Enterococcus spp.
Estudio de brotes. Responsables: Belén Aracil y María Pérez Vázquez. El programa incluye la caracterización de brotes nosocomiales y clones emergentes de alto riesgo mediante diferentes técnicas moleculares (tabla resumen). Éstas, nos permiten realizar estudios filogenéticos con el fin de obtener una información detallada acerca la relación entre los diferentes aislados y su trazabilidad. El objetivo final es generar datos que se transfieren a los hospitales como ayuda para la prevención o control de la propagación del brote.
Acreditación y Calidad. Responsable: Belén Aracil. El laboratorio Referencia e Investigación en Resistencia a Antibióticos ha sido de los primeros en el ISCIII en la utilización de técnicas acreditadas por la Entidad Nacional de Acreditaciones (ENAC). Este laboratorio consiguió la primera acreditación homologada de técnicas diagnósticas en 2012, programa que ha sido ampliado, de manera que en la actualidad más de la mitad de las técnicas ofrecidas al Sistema Nacional de Salud están debidamente acreditadas por ENAC.
Técnicos responsables de las técnicas realizadas en el Laboratorio: Noelia Lara Fuella y Verónica Bautista Sánchez.
En la siguiente imagen se resumen las técnicas ofrecidas al Sistema Nacional de Salud.
| PROGRAMAS | NOMBRE CARTERA SERVICIO | PATÓGENO | DETERMINACIÓN, DETECCIÓN, ANÁLISIS | MÉTODOS |
|
Programa de vigilancia de Haemophilus Programa de vigilancia de resistencia a antibióticos. |
Identificación bacteriana |
Haemophilus sp. Enterobacterias, gram-negativos no fermentadores, Enterococcus spp |
Identificación bacteriana |
Bioquímicos MALDI TOF Secuenciación de RNAr |
| | Identificación capsular |
Haemophilus influenzae
|
Identificación capsular fenotípica y genotípica |
Aglutinación serológica en latex PCR ind/multiplex |
| | Determinación de Sensibilidad |
Haemophilus sp. Enterobacterias, gram-negativos no fermentadores, Enterococcus
|
Determinación de Sensibilidad |
Microdilución Tiras epsilon Kirby Bauer |
| | Métodos fenotípicos de detección de mecanismos de resistencia |
Enterobacterias, gram-negativos no fermentadores,
|
Métodos fenotípicos de detección de mecanismos de resistencia |
Discos y tabletas combinados con inhibidores Tiras combinadas Test de Hodge modificado CabaNP Inmunocromatografía CBP |
| | Métodos genotípicos de detección de mecanismos de resistencia |
Haemophilus sp. Enterobacterias, gram-negativos no fermentadores, Enterococcus
|
ADN, PCR y secuenciación |
PCR ind/multiplex Análisis comparativo de las secuencias |
| | Tipificación molecular/análisis filogenéticos |
Haemophilus sp. Enterobacterias, gram-negativos no fermentadores, Enterococcus
|
Corte enzimas de restricción, electroforesis ADN, PCR y secuenciación Preparación de librerías y secuenciación y análisis de genomas completos |
PFGE
MLST
WGS |